Em busca dos micróbios urbanos
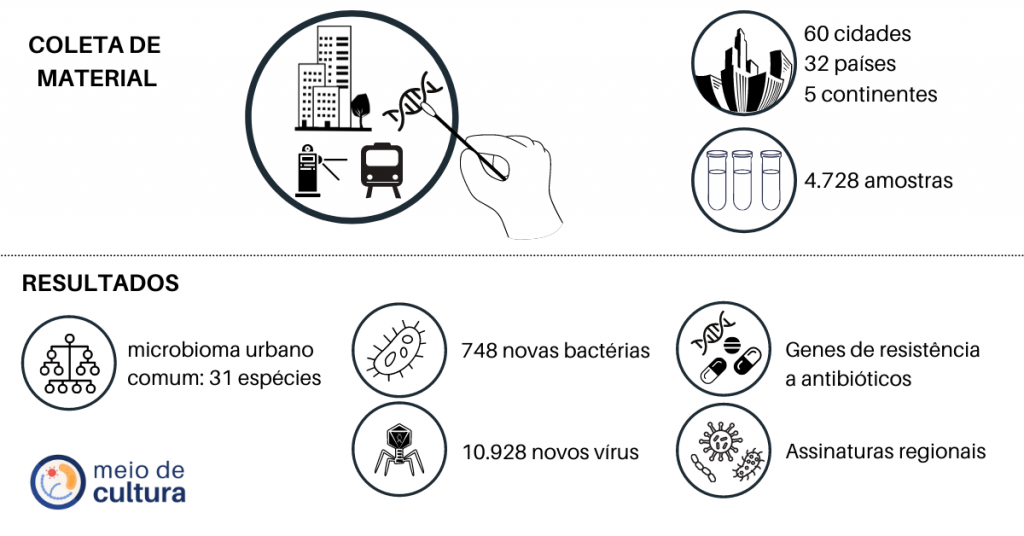
Cientistas de várias partes do mundo se uniram para um grande desafio: mapear os microrganismos das cidades! E foi uma grande colaboração, já que foram coletadas amostras em 60 cidades, de 32 países dos 5 continentes. Em 2021 o grupo publicou o que podemos chamar de o 1º Atlas Mundial de Micróbios Urbanos! Mas por que isso é importante? O que eles descobriram?
Nos últimos 20 anos, o percentual da população mundial que vive em áreas urbanizadas atingiu a marca de 55%. E, nas cidades, há um grande fluxo de pessoas que se encontrando ou passam por um mesmo local. Dessa forma, fica estabelecida uma forma de interação entre seres humanos e microrganismos que, apesar de incompreendida, pode afetar a nossa saúde, já que alguns podem causar doenças ou carregarem genes de resistência a antibióticos. E conhecer isso é muito importante
No Brasil, três cidades participaram do estudo: São Paulo/SP, Ribeirão Preto/SP e Rio de Janeiro/RJ. E, dentre os pontos de coleta, como informou o pesquisador brasileiro Emmanuel Dias-Neto, à revista Pesquisa Fapesp, as amostras de São Paulo foram coletadas principalmente de bancos de praça e de parques, como o Trianon, na av. Paulista, e das dependências do Hospital A.C.Camargo. Do Rio de Janeiro, as amostras vieram de locais públicos, bicicletas de uso comum, solas de sapato, metrô e da Fundação Oswaldo Cruz (Fiocruz), enquanto em Ribeirão Preto, elas foram coletadas no campus da USP e em pontos de ônibus
Só para se ter uma ideia do tamanho dessa pesquisa, foram coletadas 4.728 amostras, em 60 cidades! Essas amostras foram processadas para que todo o DNA ali presente fosse extraído, identificado e, então, analisado em computador – o que chamamos de metagenômica. Uma grande diversidade de espécies de vírus, fungos e bactérias foi encontrada, sendo que 748 bactérias e 10.928 vírus são de espécies ainda não descritas/catalogada – ou seja: espécies novas!
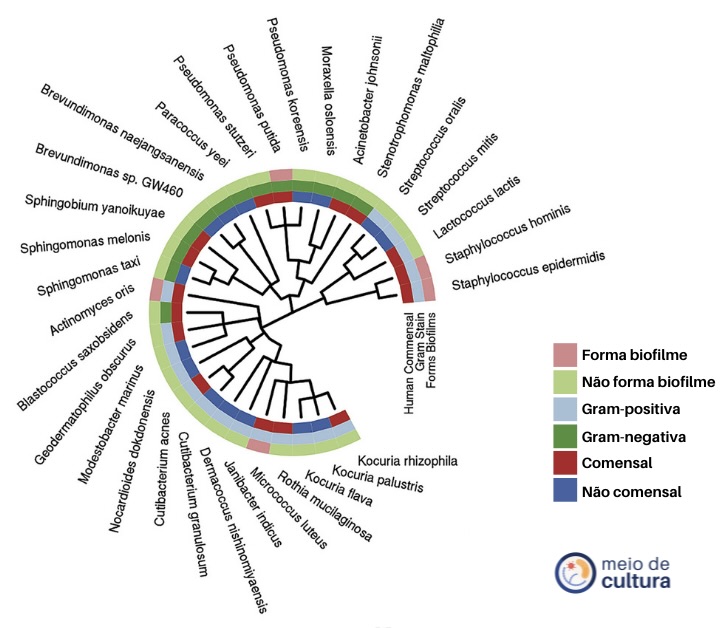
Os cientistas observaram que há um conjunto comum de 31 espécies de microrganismos que se repete em quase todas as cidades, um microbioma urbano comum.
Além disso, perceberam que há uma variação geográfica, que reflete diferenças culturais entre um local e outro. Há ainda um “efeito de vizinhança”, ou seja, quanto mais próximo, mais similaridade entre o padrão de microrganismos entre as amostras – e quanto mais longe, mais diferente. Isso é muito legal, pois mostra que há uma assinatura microbiana para cada cidade! Por exemplo, em São Paulo, temos um vírus (Meleagrid alphaherpesvirus) e duas bactérias (Pandoraea vervacti e Paraburkholderia terrae) característicos do local. Já no Rio de Janeiro, a assinatura urbana é dada pela cianobactéria (Prochlorococcus sp.) e pelos bacteriófagos Synechococcus phage.
Quem sabe, num futuro, talvez nem tão distante, você consiga dizer por onde uma pessoa passou (ou de onde vem), analisando os micróbios da sola do sapato dela! Parece brincadeira, coisa de série de investigação criminal, mas é uma aplicação forense possível e cogitada para essa descoberta!
Muitos dos grupos bacterianos identificados são frequentemente associados a quadros de infecções clínicas como Staphylococcus, Streptococcus, Corynebacterium, Klebsiella e Enterobacter. No entanto, não há evidências de que as espécies presentes naqueles ambientes também sejam patogênicas. Daí a necessidade de estudos especificamente voltados para caracterização clínica dessas amostras.
Quando falamos de genes de resistência, a distribuição acontece forma pouco uniforme. Em algumas cidades, como Bogotá, foram encontrados de 15 a 20 vezes mais genes do que a média geral. E na Oceania e no Oriente médio menos genes de resistência foram identificados. Isso pode refletir as diferentes intensidades de uso de antibióticos entre os diferentes países. Muitas vezes os genes de resistências podem ser encontrados agrupados (são o caso dos microrganismos resistentes a vários antibióticos diferentes). Então, esse alto número pode, inclusive, sugerir que pessoas podem estar entrando em contato com microrganismos multirresistentes na comunidade! O que é gravíssimo e tem aplicação e implicações clínicas muito importantes.
Materiais complementares:
Vídeo da revista Pesquisa Fapesp: – “Microrganismos estão por todos os lados (e isso não é um problema)”
Você sabe como é feita a coleta nesse tipo de experimento? Neste vídeo (em inglês) você descobre!
Referências:
Danko et al. (2021). A global metagenomic map of urban microbiomes and antimicrobial resistance. Cell, v.184(13). DOI: 10.1016/j.cell.2021.05.002
Jokura T. (2021). Os germes das metrópoles. Pesquisa Fapesp, ed.306.
Você já conhece nossas redes sociais?
Siga a gente no Twitter, no Instagram e no Facebook!
Ah! E se for fazer comprinhas na Amazon, use nosso link!